Pauli-Korrelations-Encoding zur Verkleinerung vo de Maxcut-Aaforderunge
Nutzungsschätzung: 30 Minuta auf eme Eagle r3 Prozessor (HINWEIS: Des isch bloß a Schätzung. Eure Laufzeit ka variiere.)
Hintergrund
Des Tutorial stellt Pauli-Korrelations-Encoding (PCE) [1] vor, an Aasatz zur effizienta Kodierung vo Optimierungsprobleme in Qubits für Quanteberechnunge. PCE bildet klassische Variabla in Optimierungsprobleme auf Mehrkörper-Pauli-Matrix-Korrelationä ab, was zu ara polynomiella Kompression vo de Platzaaforderunge vom Problem führt. Durch de Einsatz vo PCE wird d'Aazahl vo de für d'Kodierung benötigte Qubits reduziert, was besonders vorteilhaft isch für kurzfristige Quantegeräte mit begrenzte Qubit-Ressource. Dazu no wird analytisch nochgwiese, dass PCE inhärent Barren Plateaus abschwächt und super-polynomielle Widerstandsfähigkeit gega des Phänomen bietet. Des eigebaute Eigenschaft ermöglicht beispiellose Leischting bei Quante-Optimierungslösere.
Überblick
De PCE-Aasatz besteht aus drei Hauptschritt, wie in Abbildung 1 aus [1] unna dargestellt isch:
- Kodierung vom Optimierungsproblem in an Pauli-Korrelationsraum.
- Lösung vom Problem mit am quanta-klassische Optimierungslöser.
- Dekodierung vo de Lösung zruck in de ursprüngliche Optimierungsraum.
De PCE-Aasatz isch aapsbar aa jeden Quanta-Optimierungslöser, der Pauli-Korrelationsmatrize verarbeite ka.
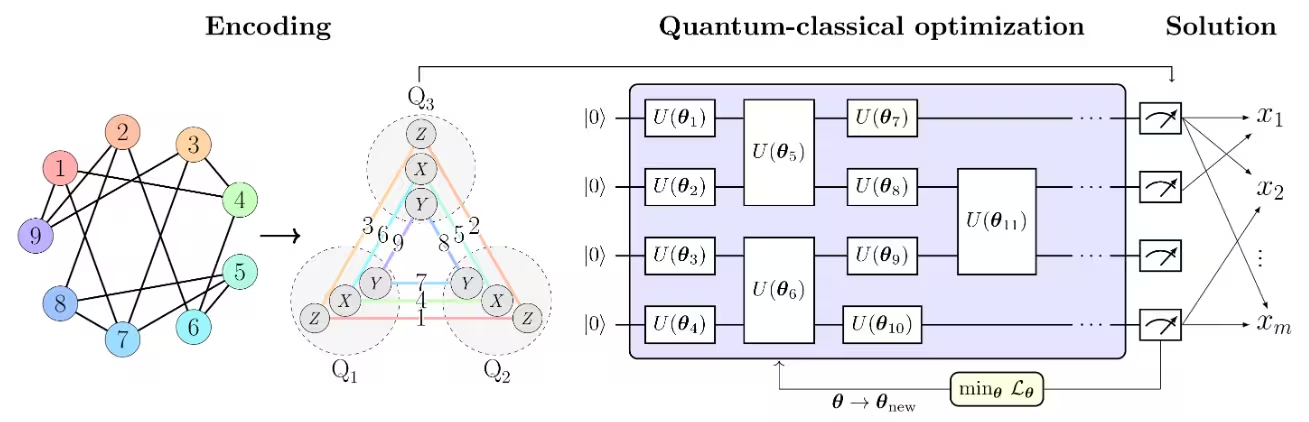 In Abbildung 1 aus [1] wird des Max-Cut-Problem als Beispiel zur Veranschaulichung vom PCE-Aasatz verwendet. Des Max-Cut-Problem mit Knota wird in an Pauli-Korrelationsraum kodiert, wobei des Optimierungsproblem als Korrelationsmatrix dargestellt wird, insbesondere als 2-Körper-Pauli-Matrix-Korrelationä über Qubits . Knotafarba gänd de Pauli-String aa, der für jeden kodierta Knota verwendet wird.
Zum Beispiel wird Knota 1, der de binära Variabla entspricht, durch de Erwartungswert von kodiert, während durch kodiert wird.
Des entspricht ara Kompression vo de Variabla vom Problem in Qubits. Allgemeiner ermöglicht -Körper-Korrelationä polynomielle Kompressiona vo de Ordnung . De gwählte Pauli-Satz umfasst drei Teilmenge vo gegaseitig kommutierenda Pauli-Strings, wodurch all Korrelationä experimentell mit bloß drei Messeinstellunge gschätzt werra könnet.
In Abbildung 1 aus [1] wird des Max-Cut-Problem als Beispiel zur Veranschaulichung vom PCE-Aasatz verwendet. Des Max-Cut-Problem mit Knota wird in an Pauli-Korrelationsraum kodiert, wobei des Optimierungsproblem als Korrelationsmatrix dargestellt wird, insbesondere als 2-Körper-Pauli-Matrix-Korrelationä über Qubits . Knotafarba gänd de Pauli-String aa, der für jeden kodierta Knota verwendet wird.
Zum Beispiel wird Knota 1, der de binära Variabla entspricht, durch de Erwartungswert von kodiert, während durch kodiert wird.
Des entspricht ara Kompression vo de Variabla vom Problem in Qubits. Allgemeiner ermöglicht -Körper-Korrelationä polynomielle Kompressiona vo de Ordnung . De gwählte Pauli-Satz umfasst drei Teilmenge vo gegaseitig kommutierenda Pauli-Strings, wodurch all Korrelationä experimentell mit bloß drei Messeinstellunge gschätzt werra könnet.
Ana Verlustfunktion vo Pauli-Erwartungswerta, die d'ursprüngliche Max-Cut-Zielfunktion nachahmt, wird konstruiert. D'Verlustfunktion wird dann mit am quanta-klassische Optimierungslöser wie dem Variational Quantum Eigensolver (VQE) optimiert.
Sobald d'Optimierung abgschlosse isch, wird d'Lösung in de ursprüngliche Optimierungsraum zurückdekodiert, wodurch d'optimale Max-Cut-Lösung errecha wird.
Aaforderunge
Stellt vor em Aafang vo dem Tutorial sicher, dass ihr des Folgende installiert hend:
- Qiskit SDK v1.0 oder höher, mit Visualisierungs-Unterstützung
- Qiskit Runtime v0.22 oder höher (
pip install qiskit-ibm-runtime)
Einrichtung
# Added by doQumentation — required packages for this notebook
!pip install -q networkx numpy qiskit qiskit-ibm-runtime rustworkx scipy
from itertools import combinations
import numpy as np
import rustworkx as rx
from scipy.optimize import minimize
from qiskit.circuit.library import efficient_su2
from qiskit.transpiler.preset_passmanagers import generate_preset_pass_manager
from qiskit.quantum_info import SparsePauliOp
from qiskit_ibm_runtime import EstimatorV2 as Estimator
from qiskit_ibm_runtime import QiskitRuntimeService
from qiskit_ibm_runtime import Session
from rustworkx.visualization import mpl_draw
service = QiskitRuntimeService()
backend = service.least_busy(
operational=True, simulator=False, min_num_qubits=127
)
def calc_cut_size(graph, partition0, partition1):
"""Calculate the cut size of the given partitions of the graph."""
cut_size = 0
for edge0, edge1 in graph.edge_list():
if edge0 in partition0 and edge1 in partition1:
cut_size += 1
elif edge0 in partition1 and edge1 in partition0:
cut_size += 1
return cut_size
Schritt 1: Klassische Eingaba auf as Quanteproblem abbilda
Max-Cut-Problem
Des Max-Cut-Problem isch a kombinatorisches Optimierungsproblem, des auf am Graphe definiert isch, wobei d'Menge vo de Knota und d'Menge vo de Kante isch. Des Ziel isch, d'Knota in zwoi Menge und z'partitioniere, sodass d'Aazahl vo de Kante zwischa de zwoi Menge maximiert wird. Für a ausführliche Beschreibung vom Max-Cut-Problem verweist bitte auf des Tutorial "Quantum approximate optimization algorithm". Außerdem wird des Max-Cut-Problem als Beispiel im Tutorial "Advanced Techniques for QAOA" verwendet. In dene Tutorials wird de QAOA-Algorithmus zur Lösung vom Max-Cut-Problem eigsetzt.
Graph -> Hamiltonian
Des Tutorial verwendet an Zufallsgraphe mit 1000 Knota.
D'Problemgröße isch möglicherweise schwer z'visualisiere, deshalb isch unna a Graph mit 100 Knota dargestellt. (D'direkte Darstellung von am Graphe mit 1.000 Knota würd'n zu dicht macha, um öppis z'sehe!) De Graph, mit dem mir arbeite, isch zehnmal größer.
mpl_draw(rx.undirected_gnp_random_graph(100, 0.1, seed=42))
num_nodes = 1000 # Number of nodes in graph
graph = rx.undirected_gnp_random_graph(num_nodes, 0.1, seed=42)
import networkx as nx
nx_graph = nx.Graph()
nx_graph.add_nodes_from(range(num_nodes))
for edge in graph.edge_list():
nx_graph.add_edge(edge[0], edge[1])
curr_cut_size, partition = nx.approximation.one_exchange(nx_graph, seed=1)
print(f"Initial cut size: {curr_cut_size}")
Initial cut size: 28075
Mir kodiere de Graphe mit 1000 Knota in 2-Körper-Pauli-Matrix-Korrelationä über 100 Qubits. De Graph wird als Korrelationsmatrix dargestellt, wobei jeder Knota durch an Pauli-String kodiert wird. Des Vorzeiche vom Erwartungswert vom Pauli-String gibt d'Partition vom Knota aa. Zum Beispiel wird Knota 0 durch an Pauli-String kodiert, . Des Vorzeiche vom Erwartungswert vo dem Pauli-String gibt d'Partition vo Knota 0 aa. Mir definiere as Pauli-Korrelations-Encoding (PCE) relativ zu als
wobei d'Partition vo Knota isch und de Erwartungswert vom Pauli-String isch, der Knota über an Quantezustand kodiert. Jetzt kodierat mir de Graphe mit PCE in an Hamiltonian. Mir teilet d'Knota in drei Menge auf: , und . Dann kodierat mir d'Knota in jedere Menge mit de Pauli-Strings , bzw. .
num_qubits = 100
list_size = num_nodes // 3
node_x = [i for i in range(list_size)]
node_y = [i for i in range(list_size, 2 * list_size)]
node_z = [i for i in range(2 * list_size, num_nodes)]
print("List 1:", node_x)
print("List 2:", node_y)
print("List 3:", node_z)
List 1: [0, 1, 2, 3, 4, 5, 6, 7, 8, 9, 10, 11, 12, 13, 14, 15, 16, 17, 18, 19, 20, 21, 22, 23, 24, 25, 26, 27, 28, 29, 30, 31, 32, 33, 34, 35, 36, 37, 38, 39, 40, 41, 42, 43, 44, 45, 46, 47, 48, 49, 50, 51, 52, 53, 54, 55, 56, 57, 58, 59, 60, 61, 62, 63, 64, 65, 66, 67, 68, 69, 70, 71, 72, 73, 74, 75, 76, 77, 78, 79, 80, 81, 82, 83, 84, 85, 86, 87, 88, 89, 90, 91, 92, 93, 94, 95, 96, 97, 98, 99, 100, 101, 102, 103, 104, 105, 106, 107, 108, 109, 110, 111, 112, 113, 114, 115, 116, 117, 118, 119, 120, 121, 122, 123, 124, 125, 126, 127, 128, 129, 130, 131, 132, 133, 134, 135, 136, 137, 138, 139, 140, 141, 142, 143, 144, 145, 146, 147, 148, 149, 150, 151, 152, 153, 154, 155, 156, 157, 158, 159, 160, 161, 162, 163, 164, 165, 166, 167, 168, 169, 170, 171, 172, 173, 174, 175, 176, 177, 178, 179, 180, 181, 182, 183, 184, 185, 186, 187, 188, 189, 190, 191, 192, 193, 194, 195, 196, 197, 198, 199, 200, 201, 202, 203, 204, 205, 206, 207, 208, 209, 210, 211, 212, 213, 214, 215, 216, 217, 218, 219, 220, 221, 222, 223, 224, 225, 226, 227, 228, 229, 230, 231, 232, 233, 234, 235, 236, 237, 238, 239, 240, 241, 242, 243, 244, 245, 246, 247, 248, 249, 250, 251, 252, 253, 254, 255, 256, 257, 258, 259, 260, 261, 262, 263, 264, 265, 266, 267, 268, 269, 270, 271, 272, 273, 274, 275, 276, 277, 278, 279, 280, 281, 282, 283, 284, 285, 286, 287, 288, 289, 290, 291, 292, 293, 294, 295, 296, 297, 298, 299, 300, 301, 302, 303, 304, 305, 306, 307, 308, 309, 310, 311, 312, 313, 314, 315, 316, 317, 318, 319, 320, 321, 322, 323, 324, 325, 326, 327, 328, 329, 330, 331, 332]
List 2: [333, 334, 335, 336, 337, 338, 339, 340, 341, 342, 343, 344, 345, 346, 347, 348, 349, 350, 351, 352, 353, 354, 355, 356, 357, 358, 359, 360, 361, 362, 363, 364, 365, 366, 367, 368, 369, 370, 371, 372, 373, 374, 375, 376, 377, 378, 379, 380, 381, 382, 383, 384, 385, 386, 387, 388, 389, 390, 391, 392, 393, 394, 395, 396, 397, 398, 399, 400, 401, 402, 403, 404, 405, 406, 407, 408, 409, 410, 411, 412, 413, 414, 415, 416, 417, 418, 419, 420, 421, 422, 423, 424, 425, 426, 427, 428, 429, 430, 431, 432, 433, 434, 435, 436, 437, 438, 439, 440, 441, 442, 443, 444, 445, 446, 447, 448, 449, 450, 451, 452, 453, 454, 455, 456, 457, 458, 459, 460, 461, 462, 463, 464, 465, 466, 467, 468, 469, 470, 471, 472, 473, 474, 475, 476, 477, 478, 479, 480, 481, 482, 483, 484, 485, 486, 487, 488, 489, 490, 491, 492, 493, 494, 495, 496, 497, 498, 499, 500, 501, 502, 503, 504, 505, 506, 507, 508, 509, 510, 511, 512, 513, 514, 515, 516, 517, 518, 519, 520, 521, 522, 523, 524, 525, 526, 527, 528, 529, 530, 531, 532, 533, 534, 535, 536, 537, 538, 539, 540, 541, 542, 543, 544, 545, 546, 547, 548, 549, 550, 551, 552, 553, 554, 555, 556, 557, 558, 559, 560, 561, 562, 563, 564, 565, 566, 567, 568, 569, 570, 571, 572, 573, 574, 575, 576, 577, 578, 579, 580, 581, 582, 583, 584, 585, 586, 587, 588, 589, 590, 591, 592, 593, 594, 595, 596, 597, 598, 599, 600, 601, 602, 603, 604, 605, 606, 607, 608, 609, 610, 611, 612, 613, 614, 615, 616, 617, 618, 619, 620, 621, 622, 623, 624, 625, 626, 627, 628, 629, 630, 631, 632, 633, 634, 635, 636, 637, 638, 639, 640, 641, 642, 643, 644, 645, 646, 647, 648, 649, 650, 651, 652, 653, 654, 655, 656, 657, 658, 659, 660, 661, 662, 663, 664, 665]
List 3: [666, 667, 668, 669, 670, 671, 672, 673, 674, 675, 676, 677, 678, 679, 680, 681, 682, 683, 684, 685, 686, 687, 688, 689, 690, 691, 692, 693, 694, 695, 696, 697, 698, 699, 700, 701, 702, 703, 704, 705, 706, 707, 708, 709, 710, 711, 712, 713, 714, 715, 716, 717, 718, 719, 720, 721, 722, 723, 724, 725, 726, 727, 728, 729, 730, 731, 732, 733, 734, 735, 736, 737, 738, 739, 740, 741, 742, 743, 744, 745, 746, 747, 748, 749, 750, 751, 752, 753, 754, 755, 756, 757, 758, 759, 760, 761, 762, 763, 764, 765, 766, 767, 768, 769, 770, 771, 772, 773, 774, 775, 776, 777, 778, 779, 780, 781, 782, 783, 784, 785, 786, 787, 788, 789, 790, 791, 792, 793, 794, 795, 796, 797, 798, 799, 800, 801, 802, 803, 804, 805, 806, 807, 808, 809, 810, 811, 812, 813, 814, 815, 816, 817, 818, 819, 820, 821, 822, 823, 824, 825, 826, 827, 828, 829, 830, 831, 832, 833, 834, 835, 836, 837, 838, 839, 840, 841, 842, 843, 844, 845, 846, 847, 848, 849, 850, 851, 852, 853, 854, 855, 856, 857, 858, 859, 860, 861, 862, 863, 864, 865, 866, 867, 868, 869, 870, 871, 872, 873, 874, 875, 876, 877, 878, 879, 880, 881, 882, 883, 884, 885, 886, 887, 888, 889, 890, 891, 892, 893, 894, 895, 896, 897, 898, 899, 900, 901, 902, 903, 904, 905, 906, 907, 908, 909, 910, 911, 912, 913, 914, 915, 916, 917, 918, 919, 920, 921, 922, 923, 924, 925, 926, 927, 928, 929, 930, 931, 932, 933, 934, 935, 936, 937, 938, 939, 940, 941, 942, 943, 944, 945, 946, 947, 948, 949, 950, 951, 952, 953, 954, 955, 956, 957, 958, 959, 960, 961, 962, 963, 964, 965, 966, 967, 968, 969, 970, 971, 972, 973, 974, 975, 976, 977, 978, 979, 980, 981, 982, 983, 984, 985, 986, 987, 988, 989, 990, 991, 992, 993, 994, 995, 996, 997, 998, 999]
def build_pauli_correlation_encoding(pauli, node_list, n, k=2):
pauli_correlation_encoding = []
for idx, c in enumerate(combinations(range(n), k)):
if idx >= len(node_list):
break
paulis = ["I"] * n
paulis[c[0]], paulis[c[1]] = pauli, pauli
pauli_correlation_encoding.append(("".join(paulis)[::-1], 1))
hamiltonian = []
for pauli, weight in pauli_correlation_encoding:
hamiltonian.append(SparsePauliOp.from_list([(pauli, weight)]))
return hamiltonian
pauli_correlation_encoding_x = build_pauli_correlation_encoding(
"X", node_x, num_qubits
)
pauli_correlation_encoding_y = build_pauli_correlation_encoding(
"Y", node_y, num_qubits
)
pauli_correlation_encoding_z = build_pauli_correlation_encoding(
"Z", node_z, num_qubits
)
Schritt 2: Problem für d'Ausführung auf Quante-Hardware optimiere
Quanteschaltkreis
Do wird de Zustand mit parametrisiert, und mir optimiere dene Parameter mit am variationella Aasatz.
Des Tutorial verwendet de efficient_su2 Aasatz für unsere variationella Algorithmus wega seiner Ausdrucksfähigkeit und einfache Implementierung.
Mir verwende au d'relaxierte Verlustfunktion, die später in dem Tutorial eigeführt wird.
Als Ergebnis könnet mir großskalige Probleme mit weniger Qubits und geringere Schaltkreistiefen aagehe.
# Build the quantum circuit
qc = efficient_su2(num_qubits, ["ry", "rz"], reps=2)
# Optimize the circuit
pm = generate_preset_pass_manager(optimization_level=3, backend=backend)
qc = pm.run(qc)
Verlustfunktion
Für d'Verlustfunktion verwende mir a Relaxation vo de Max-Cut-Zielfunktion wie in [1] beschriebe, die als definiert isch. Do bezeichnet des Gwicht vo de Kante und d'Partition vo Knota . D'Verlustfunktion isch gebe durch:
wobei d'Max-Cut-Zielfunktion durch glatte hyperbolische Tangente vo de Erwartungswerta vo de Pauli-Strings ersetzt wird, die d'Knota kodieret. De Regularisierungsterm und de Skalierungsfaktor , proportional zur Aazahl vo de Qubits, werra eigeführt, um d'Leischting vom Löser z'verbessere.
De Regularisierungsterm isch definiert als:
isch definiert als
wobei , und d'Aazahl vo de Knota im Graphe isch.
def loss_func_estimator(x, ansatz, hamiltonian, estimator, graph):
"""
Calculates the specified loss function for the given ansatz, Hamiltonian, and graph.
The expectation values of each Pauli string in the Hamiltonian are first obtained
by running the ansatz on the quantum backend. These expectation values are then
passed through the nonlinear function tanh(alpha * prod_i). The loss function is
subsequently computed from these transformed values.
"""
job = estimator.run(
[
(ansatz, hamiltonian[0], x),
(ansatz, hamiltonian[1], x),
(ansatz, hamiltonian[2], x),
]
)
result = job.result()
# calculate the loss function
node_exp_map = {}
idx = 0
for r in result:
for ev in r.data.evs:
node_exp_map[idx] = ev
idx += 1
loss = 0
alpha = num_qubits
for edge0, edge1 in graph.edge_list():
loss += np.tanh(alpha * node_exp_map[edge0]) * np.tanh(
alpha * node_exp_map[edge1]
)
regulation_term = 0
for i in range(len(graph.nodes())):
regulation_term += np.tanh(alpha * node_exp_map[i]) ** 2
regulation_term = regulation_term / len(graph.nodes())
regulation_term = regulation_term**2
beta = 1 / 2
v = len(graph.edges()) / 2 + (len(graph.nodes()) - 1) / 4
regulation_term = beta * v * regulation_term
loss = loss + regulation_term
global experiment_result
print(f"Iter {len(experiment_result)}: {loss}")
experiment_result.append({"loss": loss, "exp_map": node_exp_map})
return loss
Schritt 3: Ausführung mit Qiskit Primitives
In dem Tutorial setze mir max_iter=50 für d'Optimierungsschleife zu Demonstrationszwecke. Wenn mir d'Aazahl vo de Iterationä erhöhet, könnet mir bessere Ergebnisse erwarte.
pce = []
pce.append(
[op.apply_layout(qc.layout) for op in pauli_correlation_encoding_x]
)
pce.append(
[op.apply_layout(qc.layout) for op in pauli_correlation_encoding_y]
)
pce.append(
[op.apply_layout(qc.layout) for op in pauli_correlation_encoding_z]
)
# Run the optimization using Session
with Session(backend=backend) as session:
estimator = Estimator(mode=session)
experiment_result = []
def loss_func(x):
return loss_func_estimator(
x, qc, [pce[0], pce[1], pce[2]], estimator, graph
)
np.random.seed(42)
initial_params = np.random.rand(qc.num_parameters)
result = minimize(
loss_func, initial_params, method="COBYLA", options={"maxiter": 50}
)
print(result)
Iter 0: 16659.649201600296
Iter 1: 12104.242957555361
Iter 2: 6541.137221994661
Iter 3: 6650.6188244671985
Iter 4: 7033.193518185085
Iter 5: 6743.687931793412
Iter 6: 6223.574718684094
Iter 7: 6457.3302709535965
Iter 8: 6581.316449107595
Iter 9: 6365.761052029896
Iter 10: 6415.872673527322
Iter 11: 6421.996561600348
Iter 12: 6636.372822791712
Iter 13: 6965.174320702346
Iter 14: 6774.236562696287
Iter 15: 6393.837617108355
Iter 16: 6234.311401676519
Iter 17: 6518.192237615901
Iter 18: 6559.933925068997
Iter 19: 6646.157979243488
Iter 20: 6573.726111605048
Iter 21: 6190.642092901959
Iter 22: 6653.06500163594
Iter 23: 6545.713700369988
Iter 24: 6399.996441760465
Iter 25: 6115.959687941808
Iter 26: 6665.915093554849
Iter 27: 6832.882201259893
Iter 28: 6541.392749578919
Iter 29: 6813.3456910443165
Iter 30: 6460.800944368402
Iter 31: 6359.635437029245
Iter 32: 6040.891641882451
Iter 33: 6573.930674936448
Iter 34: 6668.031753293785
Iter 35: 6450.002712889748
Iter 36: 6519.8298811058075
Iter 37: 6467.134502398199
Iter 38: 6655.284651397334
Iter 39: 6371.168353987336
Iter 40: 6480.337259347923
Iter 41: 6339.256786764425
Iter 42: 6588.635046825541
Iter 43: 6617.677964971322
Iter 44: 6469.0441600679205
Iter 45: 6567.874244906106
Iter 46: 6217.899975264532
Iter 47: 6783.481394627947
Iter 48: 6813.371853626112
Iter 49: 6506.5871531488765
message: Maximum number of function evaluations has been exceeded.
success: False
status: 2
fun: 6040.891641882451
x: [ 1.375e+00 1.951e+00 ... 1.923e-01 4.087e-02]
nfev: 50
maxcv: 0.0
Schritt 4: Nachbearbeitung und Rückgab vom Ergebnis im gwünschte klassische Format
D'Partitionä vo de Knota werra durch Auswertung vom Vorzeiche vo de Erwartungswerta vo de Pauli-Strings bestimmt, die d'Knota kodieret.
# Calculate the partitions based on the final expectation values
# If the expectation value is positive, the node belongs to partition 0 (par0)
# Otherwise, the node belongs to partition 1 (par1)
par0, par1 = set(), set()
for i in experiment_result[-1]["exp_map"]:
if experiment_result[-1]["exp_map"][i] >= 0:
par0.add(i)
else:
par1.add(i)
print(par0, par1)
{0, 1, 4, 8, 9, 10, 12, 13, 14, 15, 16, 18, 25, 27, 31, 32, 34, 36, 38, 39, 40, 41, 44, 46, 47, 48, 49, 50, 51, 52, 57, 60, 61, 62, 63, 64, 65, 66, 68, 71, 79, 81, 82, 86, 88, 91, 92, 93, 94, 95, 96, 99, 100, 105, 106, 107, 112, 114, 115, 121, 123, 129, 133, 134, 145, 147, 161, 165, 166, 168, 171, 173, 184, 185, 187, 188, 192, 193, 194, 196, 197, 198, 202, 205, 206, 207, 208, 209, 210, 211, 215, 217, 218, 219, 220, 221, 225, 226, 227, 228, 229, 230, 231, 232, 233, 234, 235, 236, 238, 241, 242, 243, 244, 246, 247, 248, 249, 251, 252, 253, 255, 256, 257, 258, 259, 261, 262, 264, 265, 266, 268, 269, 270, 272, 273, 275, 276, 277, 278, 279, 281, 283, 284, 285, 286, 288, 292, 293, 294, 299, 300, 303, 305, 306, 307, 308, 310, 312, 313, 314, 316, 317, 319, 321, 326, 327, 328, 333, 336, 338, 340, 341, 342, 344, 345, 346, 349, 351, 352, 353, 356, 357, 360, 361, 362, 363, 364, 366, 368, 370, 374, 378, 379, 380, 381, 382, 383, 384, 386, 387, 388, 389, 390, 391, 393, 394, 395, 396, 397, 398, 404, 405, 406, 409, 411, 413, 415, 416, 418, 421, 425, 426, 427, 428, 429, 433, 434, 435, 437, 444, 450, 456, 457, 458, 459, 462, 463, 465, 467, 469, 470, 472, 476, 479, 484, 487, 489, 492, 493, 497, 498, 499, 502, 506, 508, 513, 516, 517, 518, 519, 521, 523, 526, 527, 528, 531, 532, 533, 535, 536, 537, 539, 540, 541, 542, 543, 544, 545, 547, 549, 550, 552, 557, 562, 563, 564, 565, 567, 568, 569, 570, 571, 572, 573, 576, 578, 579, 580, 583, 585, 587, 588, 589, 591, 595, 596, 597, 600, 602, 603, 604, 605, 606, 607, 608, 609, 610, 612, 618, 619, 623, 624, 625, 626, 627, 628, 630, 632, 636, 637, 640, 644, 646, 649, 652, 656, 657, 658, 659, 661, 662, 663, 664, 667, 669, 670, 671, 672, 674, 675, 676, 677, 678, 679, 680, 681, 682, 683, 684, 685, 686, 687, 688, 689, 690, 692, 693, 694, 695, 696, 698, 700, 701, 703, 706, 707, 708, 709, 712, 713, 714, 716, 717, 718, 719, 721, 722, 723, 724, 725, 726, 728, 730, 731, 733, 734, 735, 737, 739, 740, 741, 743, 744, 746, 748, 750, 751, 752, 753, 754, 758, 760, 761, 762, 763, 764, 765, 766, 774, 778, 780, 782, 787, 795, 800, 802, 803, 808, 809, 812, 818, 822, 825, 827, 834, 836, 840, 843, 845, 847, 850, 853, 854, 857, 858, 863, 864, 865, 866, 867, 868, 869, 870, 872, 873, 874, 875, 876, 878, 880, 881, 882, 883, 884, 885, 887, 888, 889, 890, 891, 893, 894, 895, 896, 898, 901, 902, 903, 904, 905, 907, 908, 910, 911, 912, 913, 914, 915, 916, 917, 918, 920, 921, 923, 925, 926, 928, 929, 930, 932, 934, 935, 936, 938, 939, 941, 943, 945, 946, 947, 948, 949, 953, 955, 956, 957, 958, 959, 961, 966, 975, 978, 980, 983, 988, 990, 996, 999} {2, 3, 5, 6, 7, 11, 17, 19, 20, 21, 22, 23, 24, 26, 28, 29, 30, 33, 35, 37, 42, 43, 45, 53, 54, 55, 56, 58, 59, 67, 69, 70, 72, 73, 74, 75, 76, 77, 78, 80, 83, 84, 85, 87, 89, 90, 97, 98, 101, 102, 103, 104, 108, 109, 110, 111, 113, 116, 117, 118, 119, 120, 122, 124, 125, 126, 127, 128, 130, 131, 132, 135, 136, 137, 138, 139, 140, 141, 142, 143, 144, 146, 148, 149, 150, 151, 152, 153, 154, 155, 156, 157, 158, 159, 160, 162, 163, 164, 167, 169, 170, 172, 174, 175, 176, 177, 178, 179, 180, 181, 182, 183, 186, 189, 190, 191, 195, 199, 200, 201, 203, 204, 212, 213, 214, 216, 222, 223, 224, 237, 239, 240, 245, 250, 254, 260, 263, 267, 271, 274, 280, 282, 287, 289, 290, 291, 295, 296, 297, 298, 301, 302, 304, 309, 311, 315, 318, 320, 322, 323, 324, 325, 329, 330, 331, 332, 334, 335, 337, 339, 343, 347, 348, 350, 354, 355, 358, 359, 365, 367, 369, 371, 372, 373, 375, 376, 377, 385, 392, 399, 400, 401, 402, 403, 407, 408, 410, 412, 414, 417, 419, 420, 422, 423, 424, 430, 431, 432, 436, 438, 439, 440, 441, 442, 443, 445, 446, 447, 448, 449, 451, 452, 453, 454, 455, 460, 461, 464, 466, 468, 471, 473, 474, 475, 477, 478, 480, 481, 482, 483, 485, 486, 488, 490, 491, 494, 495, 496, 500, 501, 503, 504, 505, 507, 509, 510, 511, 512, 514, 515, 520, 522, 524, 525, 529, 530, 534, 538, 546, 548, 551, 553, 554, 555, 556, 558, 559, 560, 561, 566, 574, 575, 577, 581, 582, 584, 586, 590, 592, 593, 594, 598, 599, 601, 611, 613, 614, 615, 616, 617, 620, 621, 622, 629, 631, 633, 634, 635, 638, 639, 641, 642, 643, 645, 647, 648, 650, 651, 653, 654, 655, 660, 665, 666, 668, 673, 691, 697, 699, 702, 704, 705, 710, 711, 715, 720, 727, 729, 732, 736, 738, 742, 745, 747, 749, 755, 756, 757, 759, 767, 768, 769, 770, 771, 772, 773, 775, 776, 777, 779, 781, 783, 784, 785, 786, 788, 789, 790, 791, 792, 793, 794, 796, 797, 798, 799, 801, 804, 805, 806, 807, 810, 811, 813, 814, 815, 816, 817, 819, 820, 821, 823, 824, 826, 828, 829, 830, 831, 832, 833, 835, 837, 838, 839, 841, 842, 844, 846, 848, 849, 851, 852, 855, 856, 859, 860, 861, 862, 871, 877, 879, 886, 892, 897, 899, 900, 906, 909, 919, 922, 924, 927, 931, 933, 937, 940, 942, 944, 950, 951, 952, 954, 960, 962, 963, 964, 965, 967, 968, 969, 970, 971, 972, 973, 974, 976, 977, 979, 981, 982, 984, 985, 986, 987, 989, 991, 992, 993, 994, 995, 997, 998}
Mir könnet d'Cut-Größe vom Max-Cut-Problem mit de Partitionä vo de Knota berechne.
cut_size = calc_cut_size(graph, par0, par1)
print(f"Cut size: {cut_size}")
Cut size: 24682
Sobald des Training abgschlossa isch, führe mir a Runde Single-Bit-Swap-Suche durch, um d'Lösung als klassische Nachbearbeitungsschritt z'verbessere. Bei dem Prozess vertausched mir d'Partitionä vo zwoi Knota und bewerte d'Cut-Größe. Wenn d'Cut-Größe verbessert wird, behalde mir de Tausch. Mir widerholed dene Prozess für all mögliche Knotapaare, die durch a Kante verbunde sind.
best_bits = []
cur_bits = []
for i in experiment_result[-1]["exp_map"]:
if experiment_result[-1]["exp_map"][i] >= 0:
cur_bits.append(1)
else:
cur_bits.append(0)
print(cur_bits)
[1, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 1, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 0, 0, 1, 1, 0, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 1, 0, 1, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 1, 0, 1, 1, 0, 0, 0, 1, 1, 1, 0, 1, 1, 1, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 1, 0, 1, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 0, 0, 1, 1, 0, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 0, 1, 0, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 1, 1, 1, 1, 0, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 1, 1, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 0, 1, 0, 1, 0, 0, 1, 1, 1, 0, 0, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 0, 0, 1, 0, 1, 0, 1, 1, 1, 0, 1, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 1, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 0, 0, 0, 1, 1, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 0, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 0, 0, 1, 1, 1, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 0, 1, 1, 0, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 1, 0, 0, 1, 0, 0, 1, 1, 0, 0, 1, 1, 0, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 1, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 1]
# Swap the partitions and calculate the cut size
best_cut = 0
for edge0, edge1 in graph.edge_list():
swapped_bits = cur_bits.copy()
swapped_bits[edge0], swapped_bits[edge1] = (
swapped_bits[edge1],
swapped_bits[edge0],
)
cur_partition = [set(), set()]
for i, bit in enumerate(swapped_bits):
if bit > 0:
cur_partition[0].add(i)
else:
cur_partition[1].add(i)
cut_size = calc_cut_size(graph, cur_partition[0], cur_partition[1])
if best_cut < cut_size:
best_cut = cut_size
best_bits = swapped_bits
print(best_cut, best_bits)
24733 [1, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 1, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 0, 0, 1, 1, 0, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 1, 0, 1, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 0, 0, 1, 1, 0, 1, 1, 0, 0, 0, 1, 1, 1, 0, 1, 1, 1, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 0, 0, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 1, 0, 1, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 0, 0, 0, 1, 1, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 0, 0, 1, 1, 0, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 0, 1, 0, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 1, 1, 1, 1, 0, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 1, 1, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 1, 1, 1, 1, 0, 1, 0, 1, 0, 0, 1, 1, 1, 0, 0, 1, 1, 1, 0, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 0, 0, 1, 0, 1, 0, 1, 1, 1, 0, 1, 0, 0, 0, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 0, 1, 1, 0, 0, 0, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 0, 1, 0, 1, 1, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 0, 1, 0, 0, 1, 0, 0, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 0, 0, 1, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 0, 0, 1, 1, 1, 0, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 1, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 0, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 0, 0, 1, 0, 1, 1, 0, 0, 0, 0, 1, 1, 0, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 1, 0, 0, 1, 0, 0, 1, 1, 0, 0, 1, 1, 0, 0, 0, 0, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 1, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 1, 0, 1, 1, 1, 1, 0, 1, 0, 0, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 1, 1, 1, 1, 1, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 1, 0, 1, 1, 1, 0, 1, 0, 1, 1, 1, 0, 1, 1, 0, 1, 0, 1, 0, 1, 1, 1, 1, 1, 0, 0, 0, 1, 0, 1, 1, 1, 1, 1, 0, 1, 0, 0, 0, 0, 1, 0, 0, 0, 0, 0, 0, 0, 0, 1, 0, 0, 1, 0, 1, 0, 0, 1, 0, 0, 0, 0, 1, 0, 1, 0, 0, 0, 0, 0, 1, 0, 0, 1]
Referenze
[1] Sciorilli, M., Borges, L., Patti, T. L., García-Martín, D., Camilo, G., Anandkumar, A., & Aolita, L. (2024). Towards large-scale quantum optimization solvers with few qubits. arXiv preprint arXiv:2401.09421.
Tutorial-Umfrag
Bitte nemmet an derer kurze Umfrag teil, um Feedback zu dem Tutorial z'gebe. Eure Erkenntnisse helfet uns, unsere Inhaltsagebote und Nutzerfahrung z'verbessere.